김진섭 대표는 4월 2일(목) 부터 6회에 걸쳐, 서울대병원 진단검사의학과 의국원들의 통계분석 능력 함양을 위한 맞춤 교육 이라는 주제로 R 교육을 진행할 예정입니다. 1주차 강의록을 미리 공유합니다.
시작하기 전에
R 데이터 매니지먼트 방법은 크게 3 종류가 있다.
tidyverse는 직관적인 코드를 작성할 수 있는 점을 장점으로 원래의 R 문법을 빠르게 대체하고 있다. 본 블로그에 정리 내용이 있다.
data.table 패키지는 빠른 실행속도를 장점으로 tidyverse 의 득세 속에서 살아남았으며, 역시 과거 홈페이지2에 정리한 바 있다.
본 강의는 이중 첫 번째에 해당하며 2주차에 tidyverse 를 다룰 것이다. data.table 은 이번 교육에는 포함시키지 않았는데, R에 익숙해지면서 느린 속도가 점점 거슬린다면 data.table 을 시작할 때이다.
실습은 클라우드 환경인 RStudio cloud 를 이용하여 진행한다. 회원가입 후, 아래를 따라 강의자료가 포함된 실습환경을 생성하자.
- https://rstudio.cloud 회원 가입
- https://rstudio.cloud/spaces/53975/join?access_code=kuFNlbt%2FbSj6DH%2FuppMdXzvU4e1EPrQNgNsFAQBf 들어가서 “Join Space” 클릭
- 위쪽 “Projects” 클릭 후, “New Project” 를 눌러 “New Project from Git Repo” 를 선택 후, Repo 주소 https://github.com/jinseob2kim/lecture-snuhlab 입력.
개인 PC에서 실습을 원한다면 http://www.r-project.org 와 https://rstudio.com/products/rstudio/download/#download 에서 R과 RStudio 를 설치하자.
전체 강의 일정
| 회차 | 일시 | 주제 |
|---|---|---|
| 1 | 4월 2일(목) 11-13시 | R 데이터 매니지먼트 기초 |
| 2 | 4월 14일(화) 11-13시 | R 데이터 매니지먼트 최근: tidyverse |
| 3 | 4월 28일(화) 11-13시 | R 데이터 시각화: ggplot2 |
| 4 | 5월 12일(화) 11-13시 | 의학연구에서의 기술통계 |
| 5 | 5월 26일(화) 11-13시 | 회귀분석, 생존분석 |
| 6 | 6월 9일(화) 11-13시 | R로 논문쓰기: rmarkdown |
R 기초연산 : 벡터(vector)
R 의 기본 연산단위는 벡터이며, x <- c(1, 2, 3) 은 1,2,3 으로 이루어진 길이 3인 벡터를 x 에 저장한다. 대입연산자는 = 와 <- 둘 다 가능하지만 함수의 인자로도 쓰이는 = 와 구별하기 위해 <- 를 권장한다. 자주 쓰는 연산을 실습하자.
[1] 8 10 12 14 16 18x * y[1] 7 16 27 40 55 72sqrt(x) ## root[1] 1.000000 1.414214 1.732051 2.000000 2.236068 2.449490sum(x) [1] 21diff(x) ## difference[1] 1 1 1 1 1mean(x) ## mean [1] 3.5var(x) ## variance[1] 3.5sd(x) ## standard deviation[1] 1.870829median(x) ## median[1] 3.5IQR(x) ## inter-quantile range[1] 2.5max(x) ## max value[1] 6which.max(x) ## order of max value[1] 6max(x, y) ## max value among x & y[1] 12length(x) [1] 6max(x, y) 는 x, y 각각의 최대값이 아닌, 전체에서 최대인 값 1개를 보여줌을 기억하자. 잠시 후 각각의 최대값 구하는 연습문제가 나온다.
벡터에서 특정 항목을 골라내려면 그것의 위치 혹은 조건문을 이용한다.
x[2] ## 2 번째[1] 2x[-2] ## 2 번째만 빼고[1] 1 3 4 5 6x[1:3] ## 1-3 번째[1] 1 2 3x[c(1, 2, 3)] ## 동일 [1] 1 2 3x[c(1, 3, 4, 5, 6)] ## 1, 3, 4, 5, 6 번째[1] 1 3 4 5 6x >= 4 ## 각 항목이 4 이상인지 TRUE/FALSE[1] FALSE FALSE FALSE TRUE TRUE TRUEsum(x >= 4) ## TRUE 1, FALSE 0 인식 [1] 3x[x >= 4] ## TRUE 인 것들만, 즉 4 이상인 것들 [1] 4 5 6sum(x[x >= 4]) ## 4 이상인 것들만 더하기. [1] 15[1] TRUE FALSE TRUE FALSE TRUE FALSE[1] 1 3 5벡터만들기
seq 로 일정 간격인, rep 로 항목들이 반복되는 벡터를 만들 수 있다.
v1 <- seq(-5, 5, by = .2); v1 ## Sequence [1] -5.0 -4.8 -4.6 -4.4 -4.2 -4.0 -3.8 -3.6 -3.4 -3.2 -3.0 -2.8 -2.6 -2.4 -2.2
[16] -2.0 -1.8 -1.6 -1.4 -1.2 -1.0 -0.8 -0.6 -0.4 -0.2 0.0 0.2 0.4 0.6 0.8
[31] 1.0 1.2 1.4 1.6 1.8 2.0 2.2 2.4 2.6 2.8 3.0 3.2 3.4 3.6 3.8
[46] 4.0 4.2 4.4 4.6 4.8 5.0v2 <- rep(1, 3); v2 ## Repeat[1] 1 1 1[1] 1 2 3 1 2 3[1] 1 1 2 2 3 3
for, if/else, ifelse 문
for loop 는 같은 작업을 반복할 때 이용하며 while 도 비슷한 의미이다. 예시를 통해 배워보자.
for (i in 1:3){
print(i)
}[1] 1
[1] 2
[1] 3i <- 0
for (j in c(1, 2, 4, 5, 6)){
i <- i + j
}
i[1] 18if 와 else 는 조건문을 다룬다. else 나 else if 문은 선행 조건문의 마지막과 같은 줄이어야 함을 기억하자.
x <- 5
if (x >= 3 ){
x <- x + 3
}
x[1] 8[1] "Medium"ifelse 는 벡터화된 if/else 문으로 벡터의 각 항목마다 조건문을 적용하는데, 엑셀의 if 문과 비슷하다.
x <- 1:6
y <- ifelse(x >= 4, "Yes", "No") ## ifelse (조건,참일때,거짓일때)
y[1] "No" "No" "No" "Yes" "Yes" "Yes"함수 만들기
막 R을 배우는 단계에서는 함수를 만들어 쓸 일이 거의 없겠지만, 결측치 포함된 데이터에서 평균이나 분산을 구할 때 귀찮을 수 있다. R은 결측치가 하나라도 포함되면 평균값, 분산값으로 NA를 출력하기 때문이다. 이를 해결하기 위해서라도 아래처럼 기초 함수 만드는 법은 알고 있는 것이 좋다.
[1] NA[1] 8둘 이상의 변수를 포함한 함수도 다음과 같이 만들 수 있다.
twomean <- function(x1, x2){
a <- (x1 + x2)/2
a
}
twomean(4, 6)[1] 5Apply 문 : apply, sapply, lapply
벡터를 다루는 연산을 잘 활용하면, 벡터의 각 항목에 대해 for loop 을 쓰는 것보다 간편하게 코드를 작성할 수 있다. 행렬에서 행마다 평균을 구하는 예를 살펴보자.
mat <- matrix(1:20, nrow = 4, byrow = T) ## 4행 5열, byrow = T : 행부터 채운다.
mat [,1] [,2] [,3] [,4] [,5]
[1,] 1 2 3 4 5
[2,] 6 7 8 9 10
[3,] 11 12 13 14 15
[4,] 16 17 18 19 20모든 행에 대해 for loop 을 이용, 평균을 구하여 저장하는 코드는 아래와 같다.
[1] 3 8 13 18처음에 빈 벡터를 만들고 여기에 결과를 붙여가는 모습이 번거로워 보인다. sapply 또는 lapply 를 사용하면 행 또는 열 단위 연산을 간단히 수행할 수 있다.
[1] 3 8 13 18[[1]]
[1] 3
[[2]]
[1] 8
[[3]]
[1] 13
[[4]]
[1] 18[1] 3 8 13 18처음에 빈 벡터를 만들고, 이어붙이는 과정이 생략되어 간단한 코드가 되었다. list 는 벡터보다 상위개념으로 모든 것을 담을 수 있는 큰 그릇에 비유할 수 있는데, 본 강의에서는 unlist 를 취하면 벡터나 행렬을 얻게 된다는 정도만 언급하고 넘어가겠다. 사실 행렬의 행/열 단위 연산은 apply 혹은 row***, col*** 시리즈의 함수가 따로 있어, 더 간단히 이용할 수 있다.
apply(mat, 1, mean) ## 1: 행[1] 3 8 13 18rowMeans(mat) ## 동일[1] 3 8 13 18rowSums(mat) ## 행별로 합[1] 15 40 65 90apply(mat, 2, mean) ## 2: 열[1] 8.5 9.5 10.5 11.5 12.5colMeans(mat) ## 열별로 합[1] 8.5 9.5 10.5 11.5 12.5연습문제 1
sapply나 lapply를 이용하여, 아래 두 벡터의 최대값을 각각 구하여라.
x <- 1:6
y <- 7:12멀티코어 병렬연산으로 apply 를 빠르게 수행할 수도 있는데 본 강의에서는 생략한다. 궁금하신 분은 과거 정리 내용 을 참고하기 바란다.
데이터 불러와서 작업하기
이제부터는 실제 데이터를 읽어서 그 데이터를 매니징 하는 방법을 배워보도록 하겠다.
데이터 불러오기, 저장하기
데이터를 불러오기 전에 미리 디렉토리를 지정하면 그 다음부터는 편하게 읽고 쓸 수 있다.
폴더 구분을 / 로 해야 한다는 점을 명심하자 (\\ 도 가능). R 은 유닉스 기반이기 때문이다. 이제 실습 데이터를 읽어볼텐데, 가급적이면 데이터 포맷은 csv로 만드는 것을 추천한다. 콤마로 분리된 가장 간단한 형태로, 용량도 작고 어떤 소프트웨어 에서도 읽을 수 있기 때문이다. 물론 Excel, SPSS, SAS 파일도 읽을 수 있는데, 변수명이나 값에 한글이 있으면 encoding 에러가 생길 수 있으므로 미리 처리하자.
URL 링크를 이용할 수도 있다.
ex <- read.csv("https://raw.githubusercontent.com/jinseob2kim/lecture-snuhlab/master/data/example_g1e.csv")Excel 파일은 readxl, SAS나 SPSS는 haven 패키지를 이용한다.
#install.packages(c("readxl", "haven")) ## install packages
library(readxl) ## for xlsx
ex.excel <- read_excel("example_g1e.xlsx", sheet = 1) ## 1st sheet
library(haven) ## for SAS/SPSS/STATA
ex.sas <- read_sas("example_g1e.sas7bdat") ## SAS
ex.spss <- read_sav("example_g1e.sav") ## SPSS
head(ex.spss)아래와 같이 Excel, SAS, SPSS 데이터는 read.csv 와 형태가 좀 달라보인다. 이것은 최근 R에서 인기있는 tidyverse 스타일의 데이터인데, 자세한 내용은 다음 강의에서 다룰 예정이니 일단 넘어가자.
파일 저장은 write.csv 를 이용하며, 맨 왼쪽에 나타나는 행 넘버링을 빼려면 row.names = F 옵션을 추가한다.
write.csv(ex, "example_g1e_ex.csv", row.names = F)haven 패키지에서 write_sas 나 write_sav 도 가능하다.
write_sas(ex.sas, "example_g1e_ex.sas7bdat")
write_sav(ex.spss, "example_g1e_ex.sav")읽은 데이터 살펴보기
본격적으로 데이터를 살펴보자. 데이터는 09-15년 공단 건강검진 데이터에서 실습용으로 32 명을 뽑은 자료이며, 자세한 내용은 “data/2교시 테이블 세부 레이아웃 소개(최신자료).pdf” 를 참고하자.
데이터 살펴보기
head 로 처음 6줄, tail 로 마지막 6줄을 볼 수 있다. 데이터 간단히 확인하려고 쓰인다.
str 은 head 와는 다른 방식으로 데이터를 확인한다. int 는 정수, num 은 실수형을 의미한다.
str(ex)'data.frame': 1644 obs. of 32 variables:
$ EXMD_BZ_YYYY : int 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 ...
$ RN_INDI : int 562083 334536 911867 183321 942671 979358 554112 487160 793017 219397 ...
$ HME_YYYYMM : int 200909 200911 200903 200908 200909 200912 200911 200908 200906 200912 ...
$ Q_PHX_DX_STK : int 0 0 0 NA NA NA NA NA NA 0 ...
$ Q_PHX_DX_HTDZ : int 0 0 0 NA NA NA NA NA NA 0 ...
$ Q_PHX_DX_HTN : int 1 0 0 NA NA NA NA NA NA 1 ...
$ Q_PHX_DX_DM : int 0 0 0 NA NA NA NA NA NA 0 ...
$ Q_PHX_DX_DLD : int 0 0 0 NA NA NA NA NA NA 0 ...
$ Q_PHX_DX_PTB : int NA NA NA NA NA NA NA NA NA NA ...
$ Q_HBV_AG : int 3 2 3 3 3 2 2 3 3 3 ...
$ Q_SMK_YN : int 1 1 1 1 1 1 1 1 1 1 ...
$ Q_DRK_FRQ_V09N: int 0 0 0 0 0 0 0 0 0 0 ...
$ HGHT : int 144 162 163 152 159 157 160 159 156 146 ...
$ WGHT : int 61 51 65 51 50 55 56 54 53 48 ...
$ WSTC : int 90 63 82 70 73 73 67 66 67 78 ...
$ BMI : num 29.4 19.4 24.5 22.1 19.8 22.3 21.9 21.4 21.8 22.5 ...
$ VA_LT : num 0.7 0.8 0.7 0.8 0.7 1.5 1.5 1.2 1.2 1.5 ...
$ VA_RT : num 0.8 1 0.6 0.9 0.8 1.5 1.5 1.5 1 1.5 ...
$ BP_SYS : int 120 120 130 101 132 110 119 111 138 138 ...
$ BP_DIA : int 80 80 80 62 78 70 78 60 72 84 ...
$ URN_PROT : int 1 1 1 1 1 1 1 1 1 1 ...
$ HGB : num 12.6 13.8 15 13.1 13 11.9 11.2 12.2 11 12.8 ...
$ FBS : int 117 96 118 90 92 100 84 88 74 107 ...
$ TOT_CHOL : int 264 169 216 199 162 192 152 166 155 178 ...
$ TG : int 128 92 132 100 58 109 38 42 86 87 ...
$ HDL : int 60 70 55 65 40 53 43 58 52 35 ...
$ LDL : int 179 80 134 114 111 117 101 99 85 125 ...
$ CRTN : num 0.9 0.9 0.8 0.9 0.9 0.7 0.8 1 0.6 0.7 ...
$ SGOT : int 25 18 26 18 24 15 8 16 15 21 ...
$ SGPT : int 20 15 30 14 23 12 6 11 13 21 ...
$ GGT : int 25 28 30 11 15 14 10 12 13 23 ...
$ GFR : int 59 74 79 61 49 83 97 65 96 70 ...names 로 변수들 이름을 확인할 수 있다. 공백이나 특수문자는 “.” 로 바뀌고, 이름이 같은 변수들은 뒤에 숫자가 추가되어 구별된다. read.csv(..., check.names = F) 옵션으로 원래 이름을 유지할 수 있으나 에러의 원인이 되므로 추천하지 않는다.
names(ex) [1] "EXMD_BZ_YYYY" "RN_INDI" "HME_YYYYMM" "Q_PHX_DX_STK"
[5] "Q_PHX_DX_HTDZ" "Q_PHX_DX_HTN" "Q_PHX_DX_DM" "Q_PHX_DX_DLD"
[9] "Q_PHX_DX_PTB" "Q_HBV_AG" "Q_SMK_YN" "Q_DRK_FRQ_V09N"
[13] "HGHT" "WGHT" "WSTC" "BMI"
[17] "VA_LT" "VA_RT" "BP_SYS" "BP_DIA"
[21] "URN_PROT" "HGB" "FBS" "TOT_CHOL"
[25] "TG" "HDL" "LDL" "CRTN"
[29] "SGOT" "SGPT" "GGT" "GFR" 샘플수, 변수 갯수는 dim, nrow, ncol 로 확인한다.
클래스는 class로 확인한다. read.csv 는 data.frame, Excel/SAS/SPSS 는 tibble & `data.frame 인데, data.frame 은 행렬이면서 데이터에 특화된 list, tibble 은 앞서 언급했던 tidyverse 스타일의 data.frame 인 정도만 알고 넘어가자.
summary 로 모든 변수들의 평균, 중위수, 결측치 등을 한 번에 확인할 수 있다. R은 결측치를 NA 로 표시하며, 안타깝지만 분산은 나오지 않는다.
summary(ex) EXMD_BZ_YYYY RN_INDI HME_YYYYMM Q_PHX_DX_STK
Min. :2009 Min. : 2270 Min. :200901 Min. :0.0000
1st Qu.:2010 1st Qu.: 230726 1st Qu.:201011 1st Qu.:0.0000
Median :2012 Median : 487160 Median :201210 Median :0.0000
Mean :2012 Mean : 490782 Mean :201216 Mean :0.0112
3rd Qu.:2014 3rd Qu.: 726101 3rd Qu.:201406 3rd Qu.:0.0000
Max. :2015 Max. :1010623 Max. :201512 Max. :1.0000
NA's :573
Q_PHX_DX_HTDZ Q_PHX_DX_HTN Q_PHX_DX_DM Q_PHX_DX_DLD
Min. :0.0000 Min. :0.00 Min. :0.0000 Min. :0.0000
1st Qu.:0.0000 1st Qu.:0.00 1st Qu.:0.0000 1st Qu.:0.0000
Median :0.0000 Median :0.00 Median :0.0000 Median :0.0000
Mean :0.0241 Mean :0.25 Mean :0.0693 Mean :0.0399
3rd Qu.:0.0000 3rd Qu.:0.25 3rd Qu.:0.0000 3rd Qu.:0.0000
Max. :1.0000 Max. :1.00 Max. :1.0000 Max. :1.0000
NA's :566 NA's :492 NA's :547 NA's :566
Q_PHX_DX_PTB Q_HBV_AG Q_SMK_YN Q_DRK_FRQ_V09N
Min. :0.0000 Min. :1.000 Min. :1.000 Min. :0.000
1st Qu.:0.0000 1st Qu.:2.000 1st Qu.:1.000 1st Qu.:0.000
Median :0.0000 Median :2.000 Median :1.000 Median :1.000
Mean :0.0276 Mean :2.235 Mean :1.632 Mean :1.026
3rd Qu.:0.0000 3rd Qu.:3.000 3rd Qu.:2.000 3rd Qu.:2.000
Max. :1.0000 Max. :3.000 Max. :3.000 Max. :7.000
NA's :703 NA's :2 NA's :2 NA's :6
HGHT WGHT WSTC BMI
Min. :134.0 Min. : 31.0 Min. : 57.00 Min. :12.30
1st Qu.:158.0 1st Qu.: 56.0 1st Qu.: 74.00 1st Qu.:21.50
Median :165.0 Median : 64.0 Median : 81.00 Median :23.70
Mean :164.5 Mean : 65.1 Mean : 80.69 Mean :23.92
3rd Qu.:171.0 3rd Qu.: 73.0 3rd Qu.: 87.00 3rd Qu.:26.20
Max. :188.0 Max. :118.0 Max. :114.00 Max. :37.20
VA_LT VA_RT BP_SYS BP_DIA
Min. :0.100 Min. :0.1000 Min. : 81.0 Min. : 49.0
1st Qu.:0.800 1st Qu.:0.7000 1st Qu.:110.0 1st Qu.: 70.0
Median :1.000 Median :1.0000 Median :120.0 Median : 78.0
Mean :0.984 Mean :0.9792 Mean :122.3 Mean : 76.6
3rd Qu.:1.200 3rd Qu.:1.2000 3rd Qu.:130.0 3rd Qu.: 82.0
Max. :9.900 Max. :9.9000 Max. :180.0 Max. :120.0
URN_PROT HGB FBS TOT_CHOL
Min. :1.000 Min. : 5.90 Min. : 61.00 Min. : 68.0
1st Qu.:1.000 1st Qu.:12.90 1st Qu.: 86.00 1st Qu.:170.0
Median :1.000 Median :14.10 Median : 94.00 Median :193.0
Mean :1.078 Mean :14.11 Mean : 97.23 Mean :194.9
3rd Qu.:1.000 3rd Qu.:15.40 3rd Qu.:103.00 3rd Qu.:218.0
Max. :5.000 Max. :18.30 Max. :290.00 Max. :363.0
NA's :4
TG HDL LDL CRTN
Min. : 13.0 Min. : 23.0 Min. : 19.0 Min. : 0.4000
1st Qu.: 72.0 1st Qu.: 46.0 1st Qu.: 90.0 1st Qu.: 0.8000
Median : 106.0 Median : 54.0 Median : 112.0 Median : 0.9000
Mean : 134.9 Mean : 55.9 Mean : 118.7 Mean : 0.9891
3rd Qu.: 163.0 3rd Qu.: 64.0 3rd Qu.: 134.0 3rd Qu.: 1.0000
Max. :1210.0 Max. :593.0 Max. :8100.0 Max. :16.5000
NA's :16
SGOT SGPT GGT GFR
Min. : 6.0 Min. : 3.00 Min. : 6.00 Min. : 3.00
1st Qu.: 19.0 1st Qu.: 15.00 1st Qu.: 16.00 1st Qu.: 76.00
Median : 23.0 Median : 20.00 Median : 24.50 Median : 87.00
Mean : 25.6 Mean : 25.98 Mean : 36.34 Mean : 89.74
3rd Qu.: 28.0 3rd Qu.: 30.00 3rd Qu.: 41.00 3rd Qu.:101.00
Max. :459.0 Max. :779.00 Max. :408.00 Max. :196.00
NA's :467 특정 변수 보기
data.frame 에서 특정변수는 $ 를 이용, 데이터이름$변수이름 로 확인할 수 있다. 앞서 언급했듯이 data.frame 은 행렬과 list의 성질도 갖고 있어 해당 스타일로도 가능하다.
ex$EXMD_BZ_YYYY ## data.frame style
ex[, "EXMD_BZ_YYYY"] ## matrix style
ex[["EXMD_BZ_YYYY"]] ## list style
ex[, 1] ## matrix style with order
ex[[1]] ## list style with order2개 이상 변수선택은 행렬 스타일을 이용한다.
특정 변수는 벡터형태로 나타나므로 처음에 다루었던 벡터다루기를 그대로 활용할 수 있다. 예를 들어 년도 변수인 EXMD_BZ_YYYY의 첫 50개만 확인하면 아래와 같다.
ex$EXMD_BZ_YYYY[1:50] ## data.frame style
ex[1:50, 1] ## matrix style
ex[[1]][1:50] ## list style [1] 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009
[16] 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009
[31] 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009 2009
[46] 2009 2009 2009 2009 2009unique 로 변수가 어떤 값들로 이루어져 있는지, table 로 해당 값들이 몇개씩 있는지 확인한다.
새로운 변수 만들기
연속형 변수인 BMI 에서 원하는 조건에 맞는 정보를 뽑아내는 연습을 해 보자.
mean(ex$BMI) ## mean[1] 23.92257BMI_cat <- (ex$BMI >= 25) ## TRUE of FALSE
table(BMI_cat) BMI_cat
FALSE TRUE
1077 567 [1] 1 14 18 21 23 24values <- ex$BMI[ex$BMI >= 25] ## values
head(values)[1] 29.4 27.5 27.7 28.0 30.7 25.6length(values)[1] 567BMI_HGHT_and <- (ex$BMI >= 25 & ex$HGHT >= 175) ## and
BMI_HGHT_or <- (ex$BMI >= 25 | ex$HGHT >= 175) ## or데이터에 새로운 변수로 추가하는 방법은 간단하다.
ex$zero <- 0 ## variable with 0
ex$BMI_cat <- (ex$BMI >= 25) ## T/F
ex$BMI_cat <- as.integer(ex$BMI >= 25) ## 0, 1
ex$BMI_cat <- as.character(ex$BMI >= 25) ## "0", "1"
ex$BMI_cat <- ifelse(ex$BMI >= 25, "1", "0") ## same
table(ex$BMI_cat)
0 1
1077 567 ex[, "BMI_cat"] <- (ex$BMI >= 25) ## matrix style
ex[["BMI_cat"]] <- (ex$BMI >= 25) ## list style변수 클래스 설정: 데이터 읽은 후 가장 먼저 해야할 것.
앞서 데이터의 클래스가 data.frame 임을 언급했었는데, 각 변수들도 자신의 클래스를 갖으며 대표적인 것이 숫자형(numeric), 문자형(character), 팩터(factor) 이다. 그 외 T/F 로 나타내는 논리(logical), 날짜를 나타내는 Date 클래스가 있다. 숫자는 integer(정수), numeric(실수) 이 있는데, 전부 실수형(numeric)으로 해도 상관없어 설명은 생략한다. 범주형은 character 와 factor 두 종류가 있는데, 전자는 단순 문자인 반면 후자는 레벨(level) 이 있어 reference 나 순서를 설정할 수 있다. read.csv 로 읽으면 숫자는 int/num, 문자는 전부 factor 가 기본값이므로, 숫자 변수 중 0/1 같은 것들은 직접 factor 로 바꿔줘야 한다. ID와 설문조사 변수를 범주형으로 바꿔보자.
vars.cat <- c("RN_INDI", "Q_PHX_DX_STK", "Q_PHX_DX_HTDZ", "Q_PHX_DX_HTN", "Q_PHX_DX_DM", "Q_PHX_DX_DLD", "Q_PHX_DX_PTB",
"Q_HBV_AG", "Q_SMK_YN", "Q_DRK_FRQ_V09N")
vars.cat <- names(ex)[c(2, 4:12)] ## same
vars.cat <- c("RN_INDI", grep("Q_", names(ex), value = T)) ## same: extract variables starting with "Q_"
vars.conti <- setdiff(names(ex), vars.cat) ## Exclude categorical variables
vars.conti <- names(ex)[!(names(ex) %in% vars.cat)] ## same: !- not, %in%- including
for (vn in vars.cat){ ## for loop: as.factor
ex[, vn] <- as.factor(ex[, vn])
}
for (vn in vars.conti){ ## for loop: as.numeric
ex[, vn] <- as.numeric(ex[, vn])
}
summary(ex) EXMD_BZ_YYYY RN_INDI HME_YYYYMM Q_PHX_DX_STK Q_PHX_DX_HTDZ
Min. :2009 4263 : 7 Min. :200901 0 :1059 0 :1052
1st Qu.:2010 38967 : 7 1st Qu.:201011 1 : 12 1 : 26
Median :2012 56250 : 7 Median :201210 NA's: 573 NA's: 566
Mean :2012 84322 : 7 Mean :201216
3rd Qu.:2014 99917 : 7 3rd Qu.:201406
Max. :2015 115809 : 7 Max. :201512
(Other):1602
Q_PHX_DX_HTN Q_PHX_DX_DM Q_PHX_DX_DLD Q_PHX_DX_PTB Q_HBV_AG Q_SMK_YN
0 :864 0 :1021 0 :1035 0 :915 1 : 77 1 :995
1 :288 1 : 76 1 : 43 1 : 26 2 :1102 2 :256
NA's:492 NA's: 547 NA's: 566 NA's:703 3 : 463 3 :391
NA's: 2 NA's: 2
Q_DRK_FRQ_V09N HGHT WGHT WSTC
0 :805 Min. :134.0 Min. : 31.0 Min. : 57.00
1 :379 1st Qu.:158.0 1st Qu.: 56.0 1st Qu.: 74.00
2 :249 Median :165.0 Median : 64.0 Median : 81.00
3 :121 Mean :164.5 Mean : 65.1 Mean : 80.69
4 : 28 3rd Qu.:171.0 3rd Qu.: 73.0 3rd Qu.: 87.00
(Other): 56 Max. :188.0 Max. :118.0 Max. :114.00
NA's : 6
BMI VA_LT VA_RT BP_SYS
Min. :12.30 Min. :0.100 Min. :0.1000 Min. : 81.0
1st Qu.:21.50 1st Qu.:0.800 1st Qu.:0.7000 1st Qu.:110.0
Median :23.70 Median :1.000 Median :1.0000 Median :120.0
Mean :23.92 Mean :0.984 Mean :0.9792 Mean :122.3
3rd Qu.:26.20 3rd Qu.:1.200 3rd Qu.:1.2000 3rd Qu.:130.0
Max. :37.20 Max. :9.900 Max. :9.9000 Max. :180.0
BP_DIA URN_PROT HGB FBS
Min. : 49.0 Min. :1.000 Min. : 5.90 Min. : 61.00
1st Qu.: 70.0 1st Qu.:1.000 1st Qu.:12.90 1st Qu.: 86.00
Median : 78.0 Median :1.000 Median :14.10 Median : 94.00
Mean : 76.6 Mean :1.078 Mean :14.11 Mean : 97.23
3rd Qu.: 82.0 3rd Qu.:1.000 3rd Qu.:15.40 3rd Qu.:103.00
Max. :120.0 Max. :5.000 Max. :18.30 Max. :290.00
NA's :4
TOT_CHOL TG HDL LDL
Min. : 68.0 Min. : 13.0 Min. : 23.0 Min. : 19.0
1st Qu.:170.0 1st Qu.: 72.0 1st Qu.: 46.0 1st Qu.: 90.0
Median :193.0 Median : 106.0 Median : 54.0 Median : 112.0
Mean :194.9 Mean : 134.9 Mean : 55.9 Mean : 118.7
3rd Qu.:218.0 3rd Qu.: 163.0 3rd Qu.: 64.0 3rd Qu.: 134.0
Max. :363.0 Max. :1210.0 Max. :593.0 Max. :8100.0
NA's :16
CRTN SGOT SGPT GGT
Min. : 0.4000 Min. : 6.0 Min. : 3.00 Min. : 6.00
1st Qu.: 0.8000 1st Qu.: 19.0 1st Qu.: 15.00 1st Qu.: 16.00
Median : 0.9000 Median : 23.0 Median : 20.00 Median : 24.50
Mean : 0.9891 Mean : 25.6 Mean : 25.98 Mean : 36.34
3rd Qu.: 1.0000 3rd Qu.: 28.0 3rd Qu.: 30.00 3rd Qu.: 41.00
Max. :16.5000 Max. :459.0 Max. :779.00 Max. :408.00
GFR zero BMI_cat
Min. : 3.00 Min. :0 Min. :0.0000
1st Qu.: 76.00 1st Qu.:0 1st Qu.:0.0000
Median : 87.00 Median :0 Median :0.0000
Mean : 89.74 Mean :0 Mean :0.3449
3rd Qu.:101.00 3rd Qu.:0 3rd Qu.:1.0000
Max. :196.00 Max. :0 Max. :1.0000
NA's :467 summary 를 보면 설문조사 변수들이 처음과 달리 빈도로 요약됨을 알 수 있다. 한 가지 주의할 점은 factor 를 numeric 으로 바로 바꾸면 안된다는 것이다. 방금 factor 로 바꾼 Q_PHX_DX_STK 를 numeric 으로 바꿔서 테이블로 요약하면, 원래의 0/1 이 아닌 1/2로 바뀐다.
table(
as.numeric(ex$Q_PHX_DX_STK)
)
1 2
1059 12 factor를 바로 바꾸면 원래 값이 아닌, factor에 내장된 레벨(순서값) 로 바뀌기 때문이다. 제대로 바꾸려면 아래처럼 character 로 먼저 바꿔준 후 숫자형을 적용해야 한다.
table(
as.numeric(as.character(ex$Q_PHX_DX_STK))
)
0 1
1059 12 마지막으로 Date 클래스를 살펴보자. 검진년월 변수인 HME_YYYYMM 를 Date 로 바꿔 볼텐데, Date는 년/월/일 이 모두 필요하므로 일은 1로 통일하고 paste 로 붙이겠다.
결측치 다루기
변수 클래스만큼 중요한 것이 결측치 처리이다. 앞서 “함수만들기” 에서 봤듯이 결측치가 있으면 평균같은 기본적인 계산도 na.rm = T 옵션이 필요하다. 결측치가 있는 LDL 변수의 평균을 연도별로 구해보자. 그룹별 통계는 tapply 를 이용한다.
tapply(ex$LDL, ex$EXMD_BZ_YYYY, mean) ## measure/group/function| 2009 | 2010 | 2011 | 2012 | 2013 | 2014 | 2015 |
|---|---|---|---|---|---|---|
| 150.9486 | NA | NA | NA | NA | NA | NA |
2009년만 결측치가 없고, 나머지는 결측치가 있어 평균값이 NA 로 나온다.na.rm = T 옵션으로 결측치를 제외하면 원하는 결과를 얻는다.
2009 2010 2011 2012 2013 2014 2015
150.9486 112.9914 112.9450 117.5259 111.1577 116.5455 111.5294 더 큰 문제는, 대부분의 R 통계분석이 결측치를 갖는 샘플을 분석에서 제외한다는 점이다. 그래서 결측치를 신경쓰지 않고 분석하다보면, 원래 샘플 수와 분석에 이용된 샘플 수가 달라지는 문제가 생길 수 있다. LDL과 HDL 의 회귀분석 결과를 예로 살펴보자.
Call:
lm(formula = LDL ~ HDL, data = ex)
Residuals:
Min 1Q Median 3Q Max
-103.8 -28.2 -6.6 15.4 7974.7
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 138.2747 15.2318 9.078 <2e-16 ***
HDL -0.3499 0.2570 -1.362 0.174
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1
Residual standard error: 201.9 on 1626 degrees of freedom
(16 observations deleted due to missingness)
Multiple R-squared: 0.001139, Adjusted R-squared: 0.0005244
F-statistic: 1.854 on 1 and 1626 DF, p-value: 0.1735“16 observations deleted due to missingness” 라는 글자가 보일 것이다. LDL 이 결측인 16명은 분석에서 제외했다는 뜻이다.
연습문제 2: 결측치 처리
결측치를 처리하는 제일 간단한 방법은 “하나라도 결측치 있는 샘플은 제외” 로, na.omit 함수를 이용하면 된다.
1644 명에서 620 명으로 샘플 수가 줄어든 것을 확인할 수 있다. 필자는 보통 결측치 처리에 다음의 3가지 원칙을 적용한다.
결측치 너무 많으면(예: 10% 이상) 그 변수는 삭제
연속변수는 중간값(median)
범주형변수는 최빈값(mode)
이제 문제이다. 아까 변수형을 정리한 ex 데이터에 위 3가지 원칙을 적용, 새로운 데이터 ex.impute 을 만들어 보아라. 단 최빈값 함수는 아래와 같이 getmode 로 주어진다.
[1] 0
Levels: 0 1정답 보기
vars.ok <- sapply(names(ex), function(v){sum(is.na(ex[, v])) < nrow(ex)/10})
ex.impute <- ex[, vars.ok] ## only missing < 10%
for (v in names(ex.impute)){
if (is.factor(ex.impute[, v])){ ## or class(ex[, v]) == "factor"
ex.impute[, v] <- ifelse(is.na(ex.impute[, v]),
getmode(ex.impute[, v]),
ex.impute[, v])
} else if (is.numeric(ex[, v])){ ## or class(ex[, v]) %in% c("integer", "numeric")
ex.impute[, v] <- ifelse(is.na(ex.impute[, v]),
median(ex.impute[, v], na.rm = T),
ex.impute[, v])
} else{ ## when date
ex.impute[, v]
}
}
summary(ex.impute) EXMD_BZ_YYYY RN_INDI HME_YYYYMM Q_HBV_AG
Min. :2009 Min. : 1.0 Min. :2009-01-01 Min. :1.000
1st Qu.:2010 1st Qu.:133.8 1st Qu.:2010-11-01 1st Qu.:2.000
Median :2012 Median :275.0 Median :2012-10-01 Median :2.000
Mean :2012 Mean :272.7 Mean :2012-08-31 Mean :2.235
3rd Qu.:2014 3rd Qu.:405.2 3rd Qu.:2014-06-01 3rd Qu.:3.000
Max. :2015 Max. :547.0 Max. :2015-12-01 Max. :3.000
Q_SMK_YN Q_DRK_FRQ_V09N HGHT WGHT
Min. :1.000 Min. :1.000 Min. :134.0 Min. : 31.0
1st Qu.:1.000 1st Qu.:1.000 1st Qu.:158.0 1st Qu.: 56.0
Median :1.000 Median :2.000 Median :165.0 Median : 64.0
Mean :1.631 Mean :2.023 Mean :164.5 Mean : 65.1
3rd Qu.:2.000 3rd Qu.:3.000 3rd Qu.:171.0 3rd Qu.: 73.0
Max. :3.000 Max. :8.000 Max. :188.0 Max. :118.0
WSTC BMI VA_LT VA_RT
Min. : 57.00 Min. :12.30 Min. :0.100 Min. :0.1000
1st Qu.: 74.00 1st Qu.:21.50 1st Qu.:0.800 1st Qu.:0.7000
Median : 81.00 Median :23.70 Median :1.000 Median :1.0000
Mean : 80.69 Mean :23.92 Mean :0.984 Mean :0.9792
3rd Qu.: 87.00 3rd Qu.:26.20 3rd Qu.:1.200 3rd Qu.:1.2000
Max. :114.00 Max. :37.20 Max. :9.900 Max. :9.9000
BP_SYS BP_DIA URN_PROT HGB
Min. : 81.0 Min. : 49.0 Min. :1.000 Min. : 5.90
1st Qu.:110.0 1st Qu.: 70.0 1st Qu.:1.000 1st Qu.:12.90
Median :120.0 Median : 78.0 Median :1.000 Median :14.10
Mean :122.3 Mean : 76.6 Mean :1.078 Mean :14.11
3rd Qu.:130.0 3rd Qu.: 82.0 3rd Qu.:1.000 3rd Qu.:15.40
Max. :180.0 Max. :120.0 Max. :5.000 Max. :18.30
FBS TOT_CHOL TG HDL
Min. : 61.00 Min. : 68.0 Min. : 13.0 Min. : 23.0
1st Qu.: 86.00 1st Qu.:170.0 1st Qu.: 72.0 1st Qu.: 46.0
Median : 94.00 Median :193.0 Median : 106.0 Median : 54.0
Mean : 97.23 Mean :194.9 Mean : 134.9 Mean : 55.9
3rd Qu.:103.00 3rd Qu.:218.0 3rd Qu.: 163.0 3rd Qu.: 64.0
Max. :290.00 Max. :363.0 Max. :1210.0 Max. :593.0
LDL CRTN SGOT SGPT
Min. : 19.0 Min. : 0.4000 Min. : 6.0 Min. : 3.00
1st Qu.: 90.0 1st Qu.: 0.8000 1st Qu.: 19.0 1st Qu.: 15.00
Median : 112.0 Median : 0.9000 Median : 23.0 Median : 20.00
Mean : 118.6 Mean : 0.9891 Mean : 25.6 Mean : 25.98
3rd Qu.: 134.0 3rd Qu.: 1.0000 3rd Qu.: 28.0 3rd Qu.: 30.00
Max. :8100.0 Max. :16.5000 Max. :459.0 Max. :779.00
GGT zero BMI_cat
Min. : 6.00 Min. :0 Min. :0.0000
1st Qu.: 16.00 1st Qu.:0 1st Qu.:0.0000
Median : 24.50 Median :0 Median :0.0000
Mean : 36.34 Mean :0 Mean :0.3449
3rd Qu.: 41.00 3rd Qu.:0 3rd Qu.:1.0000
Max. :408.00 Max. :0 Max. :1.0000 Subset
특정 조건을 만족하는 서브데이터는 지금까지 배웠던 것을 응용해 만들 수도 있지만, subset 함수가 편하다. 아래는 2012 이후의 자료만 뽑는 예시이다. 이제부터는 결측치를 전부 제외한 ex.naomit 데이터를 이용하겠다.
그룹별 통계
결측치 다루기에서 그룹별 통계를 구할 때 tapply 를 이용했었다. tapply 를 여러 변수, 여러 그룹을 동시에 고려도록 확장할 수 있는 함수가 aggregate 로, 허리둘레와 BMI의 평균을 고혈압 또는 당뇨 여부에 따라 살펴보자.
| Group.1 | WSTC | BMI |
|---|---|---|
| 0 | 80.35687 | 23.85592 |
| 1 | 84.48958 | 25.11771 |
| Q_PHX_DX_HTN | WSTC | BMI |
|---|---|---|
| 0 | 80.35687 | 23.85592 |
| 1 | 84.48958 | 25.11771 |
결측치가 있어도 잘 적용된다는 장점이 있다.
| Q_PHX_DX_HTN | WSTC | BMI |
|---|---|---|
| 0 | 80.23958 | 23.70961 |
| 1 | 83.87847 | 24.99861 |
당뇨여부도 그룹으로 다루려면 list 에 추가하면 된다.
| Group.1 | Group.2 | WSTC | BMI |
|---|---|---|---|
| 0 | 0 | 80.23107 | 23.82990 |
| 1 | 0 | 83.93976 | 25.17952 |
| 0 | 1 | 87.55556 | 25.34444 |
| 1 | 1 | 88.00000 | 24.72308 |
Group.1 이 첫번째 그룹은 고혈압 여부, Group.2 가 두번째 그룹인 당뇨 여부이다. 위와 마찬가지로 formula 형태를 이용할 수도 있다.
| Q_PHX_DX_HTN | Q_PHX_DX_DM | WSTC | BMI |
|---|---|---|---|
| 0 | 0 | 80.23107 | 23.82990 |
| 1 | 0 | 83.93976 | 25.17952 |
| 0 | 1 | 87.55556 | 25.34444 |
| 1 | 1 | 88.00000 | 24.72308 |
표준편차를 같이 보려면 function(x){c(mean = mean(x), sd = sd(x))} 와 같이 원하는 함수들을 벡터로 모으면 된다.
Warning in `[<-.data.frame`(`*tmp*`, , isn, value = structure(list(WSTC.mean =
c("80.231068", : provided 4 variables to replace 2 variables| Q_PHX_DX_HTN | Q_PHX_DX_DM | WSTC | BMI |
|---|---|---|---|
| 0 | 0 | 80.231068 | 9.546884 |
| 1 | 0 | 83.939759 | 9.124277 |
| 0 | 1 | 87.555556 | 7.551674 |
| 1 | 1 | 88.000000 | 6.177918 |
아예 데이터의 모든 변수의 평균을 다 볼순 없을까? 아래처럼 “.” 으로 전체 데이터를 지정할 수 있다.
Q_PHX_DX_HTN Q_PHX_DX_DM EXMD_BZ_YYYY.mean EXMD_BZ_YYYY.sd RN_INDI.mean
1 0 0 2013.493204 1.109498 269.30680
2 1 0 2013.578313 1.105645 251.78313
3 0 1 2013.333333 1.414214 269.77778
4 1 1 2013.307692 1.031553 303.53846
RN_INDI.sd HME_YYYYMM.mean HME_YYYYMM.sd Q_PHX_DX_STK.mean Q_PHX_DX_STK.sd
1 159.12594 16102.3184 422.8574 1.00776699 0.08787296
2 154.03951 16121.8072 413.1641 1.01204819 0.10976426
3 92.88807 16036.3333 551.2248 1.00000000 0.00000000
4 142.18686 16018.6923 417.4666 1.07692308 0.27735010
Q_PHX_DX_HTDZ.mean Q_PHX_DX_HTDZ.sd Q_PHX_DX_DLD.mean Q_PHX_DX_DLD.sd
1 1.00194175 0.04406526 1.0174757 0.1311630
2 1.06024096 0.23937916 1.0722892 0.2605404
3 1.00000000 0.00000000 1.0000000 0.0000000
4 1.07692308 0.27735010 1.0769231 0.2773501
Q_PHX_DX_PTB.mean Q_PHX_DX_PTB.sd Q_HBV_AG.mean Q_HBV_AG.sd Q_SMK_YN.mean
1 1.0271845 0.1627787 2.2291262 0.5236863 1.6970874
2 1.0000000 0.0000000 2.1927711 0.5512255 1.3855422
3 1.0000000 0.0000000 2.0000000 0.0000000 1.6666667
4 1.0769231 0.2773501 2.2307692 0.4385290 1.5384615
Q_SMK_YN.sd Q_DRK_FRQ_V09N.mean Q_DRK_FRQ_V09N.sd HGHT.mean HGHT.sd
1 0.8674234 2.0388350 1.3329287 166.613592 9.116636
2 0.6777172 1.9759036 1.3612754 160.506024 9.254364
3 0.8660254 1.8888889 0.3333333 168.333333 10.185774
4 0.6602253 1.9230769 1.1151636 162.384615 9.639662
WGHT.mean WGHT.sd WSTC.mean WSTC.sd BMI.mean BMI.sd VA_LT.mean
1 66.582524 13.211630 80.231068 9.546884 23.829903 3.276315 1.0190291
2 65.313253 13.155661 83.939759 9.124277 25.179518 3.693922 0.8469880
3 71.777778 8.913161 87.555556 7.551674 25.344444 2.711140 0.9111111
4 65.076923 6.211032 88.000000 6.177918 24.723077 2.057164 0.7769231
VA_LT.sd VA_RT.mean VA_RT.sd BP_SYS.mean BP_SYS.sd BP_DIA.mean BP_DIA.sd
1 0.5248189 1.0079612 0.3503677 119.889320 13.378266 75.452427 9.464616
2 0.3201895 0.8638554 0.3444962 132.879518 14.344539 81.481928 11.015910
3 0.1691482 0.8111111 0.2368778 128.555556 8.647415 83.333333 11.842719
4 0.2350668 0.9000000 0.1080123 129.461538 12.149180 79.307692 7.846280
URN_PROT.mean URN_PROT.sd HGB.mean HGB.sd FBS.mean FBS.sd
1 1.0543689 0.3430173 14.3749515 1.5952305 94.75534 12.71807
2 1.2168675 0.6634756 14.1048193 1.6682036 103.60241 14.34330
3 1.0000000 0.0000000 15.2555556 1.0284832 131.11111 19.62425
4 1.0769231 0.2773501 13.4153846 0.9711215 125.30769 34.11838
TOT_CHOL.mean TOT_CHOL.sd TG.mean TG.sd HDL.mean HDL.sd LDL.mean
1 196.96505 34.20684 132.80777 107.56421 54.943689 12.881333 118.49903
2 191.30120 32.64769 138.09639 81.93106 55.903614 16.123468 108.22892
3 169.77778 47.79325 164.66667 68.40870 46.333333 9.394147 92.77778
4 179.61538 39.92397 154.76923 139.23072 48.769231 10.288779 102.30769
LDL.sd CRTN.mean CRTN.sd SGOT.mean SGOT.sd SGPT.mean SGPT.sd
1 50.86475 0.8871845 0.1867988 24.151456 9.426161 24.609709 16.616090
2 29.09167 0.9168675 0.2483208 25.289157 6.400324 22.963855 9.671993
3 38.88694 0.9666667 0.2549510 35.777778 25.849457 47.666667 44.235167
4 28.39420 0.9153846 0.1675617 31.769231 19.689904 36.307692 27.417709
GGT.mean GGT.sd GFR.mean GFR.sd zero.mean zero.sd BMI_cat.mean BMI_cat.sd
1 34.47573 31.35216 92.01359 19.14246 0 0 0.3223301 0.4678230
2 35.77108 31.18799 81.16867 17.75430 0 0 0.4337349 0.4986022
3 44.22222 21.01058 87.55556 22.20423 0 0 0.5555556 0.5270463
4 48.46154 66.83265 80.69231 14.34332 0 0 0.1538462 0.3755338Sort
정렬은 순위함수인 order 를 이용한다. 기본은 오름차순이며, 내림차순을 원한다면 (-) 붙인 값의 순위를 구하면 된다.
[1] 500 168 3 328 473 177head(ex1$HGHT[ord]) ## Sort[1] 138 139 140 140 141 143[1] 188 186 185 185 184 183ex1.sort <- ex1[ord, ]
head(ex1.sort)Wide to long, long to wide format
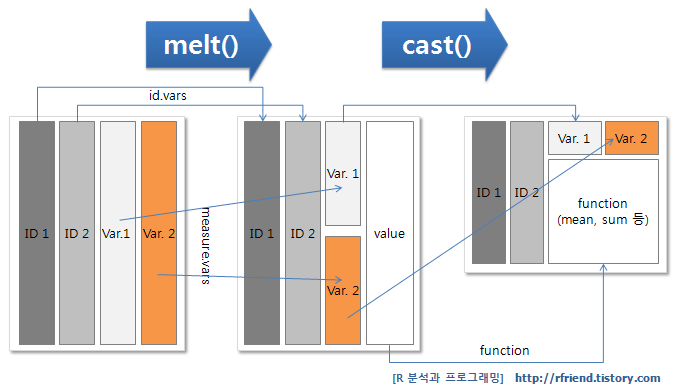
받은 데이터가 원하는 형태가 아닌 경우가 있다. 수축기 혈압을 10번 측정해서 각각 SBP1, SBP2, …, SBP10 변수에 기록된 데이터를 본다면, 이것들을 쫙 아래로 내려 측정시기, 측정값 2개의 변수로 정리하고 싶다는 마음이 들 것이다. 이럴 때 쓰는 함수가 melt, 반대로 데이터를 옆으로 늘릴 때 쓰는 함수가 dcast 이다(Figure @ref(fig:melt)3).
실습으로 수축기/이완기 혈압 변수를 합쳐서 아래로 내려보자.
id 는 유지할 변수, measure.vars 는 내릴 변수를 의미하고, variable.name, value.name 은 각각 그룹, 값의 변수이름을 의미한다. 이를 원래대로 되돌리려면 dcast 를 이용하는데, “유지할 변수 ~ 펼칠 변수” 형태로 formula 를 입력한다.
wide <- dcast(long, EXMD_BZ_YYYY + RN_INDI ~ BP_type, value.var = "BP")
head(wide)Merge
merge 함수를 이용한다. “by” 옵션으로 기준이 되는 공통 컬럼을 설정하며, 기준 컬럼의 이름이 두 데이터 셋에서 다른 경우는 “by.x” 와 “by.y” 로 따로 설정한다. 실습을 위해 ex1 데이터를 2개로 나눈 후 merge 를 적용하겠다.
전자는 설문조사 결과를, 후자는 측정값을 포함했고 “년도, ID, 검진년월” 은 공통변수이다. 이 공통변수로 merge 를 적용하면
합쳐진 원래 데이터를 얻을 수 있다. all = T 는 한 쪽에만 있는 샘플을 유지하는 옵션이며 빈 변수는 NA 로 채워진다. 공통인 샘플만 취하려면 all = F 로 바꾸자.
마치며
이번 강의를 정리하자.
RStudio cloud 로 클라우드 환경에서 실습을 진행했으며
기초 벡터연산과
for,if,ifelse,함수만들기,apply문을 통해 기본 문법을 익혔고-
공단 검진 데이터를 실습자료를 읽어와 데이터를 살펴보는 법을 배웠다.
- 변수 생성, 클래스 설정, 결측치 처리, 서브데이터, 그룹별 통계, 정렬
마지막으로 Long/wide type 데이터 변환과
merge를 다루었다.
기타 기본적으로 알아야 할 R 명령어는 아래의 Base R Cheat Sheet 에서 확인할 수 있다.
Footnotes
Citation
@online{kim2020,
author = {Kim, Jinseob},
title = {R {데이터} {매니지먼트:} {기초}},
date = {2020-03-10},
url = {https://blog.zarathu.com/posts/2020-02-16-rdatamanagement-basic/},
langid = {en}
}